这是一个创建于 57 天前的主题,其中的信息可能已经有所发展或是发生改变。
原文链接: https://nph.onlinelibrary.wiley.com/doi/10.1111/nph.18546


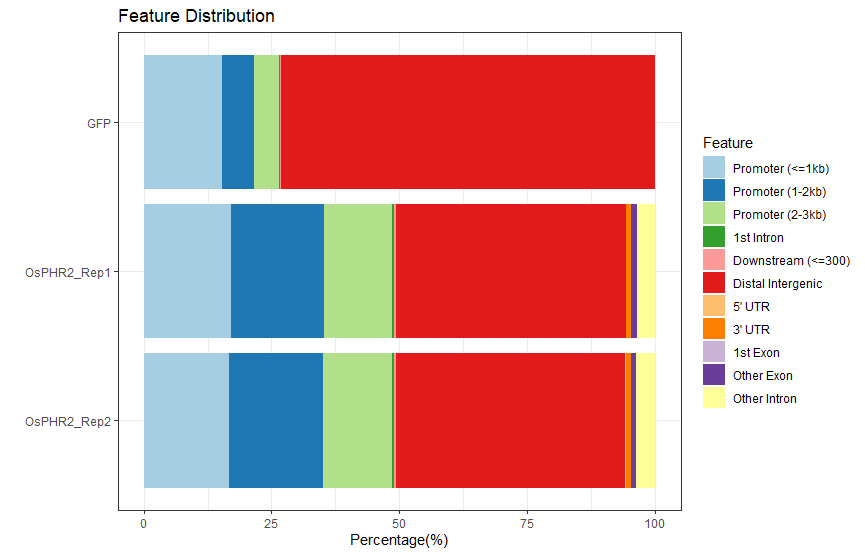
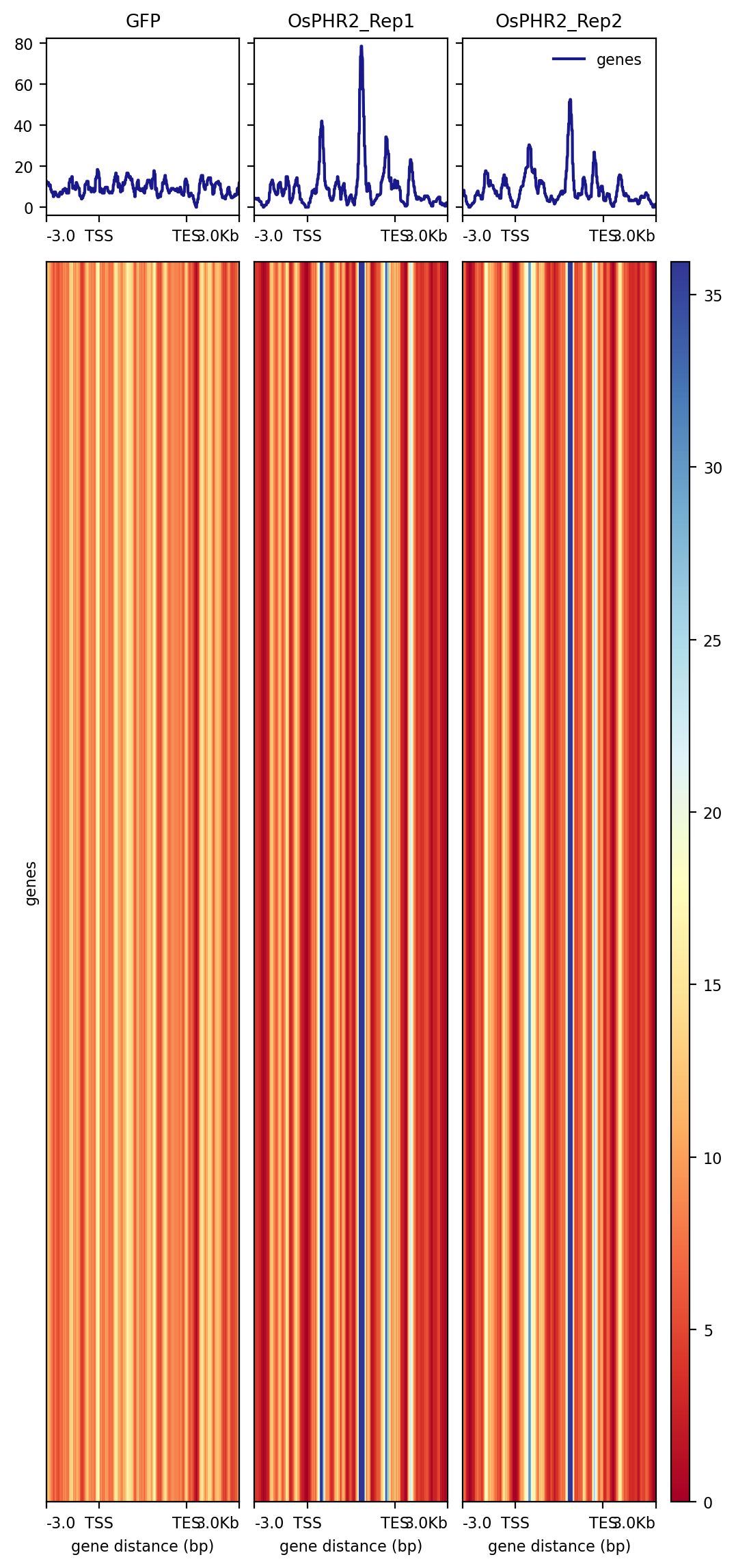
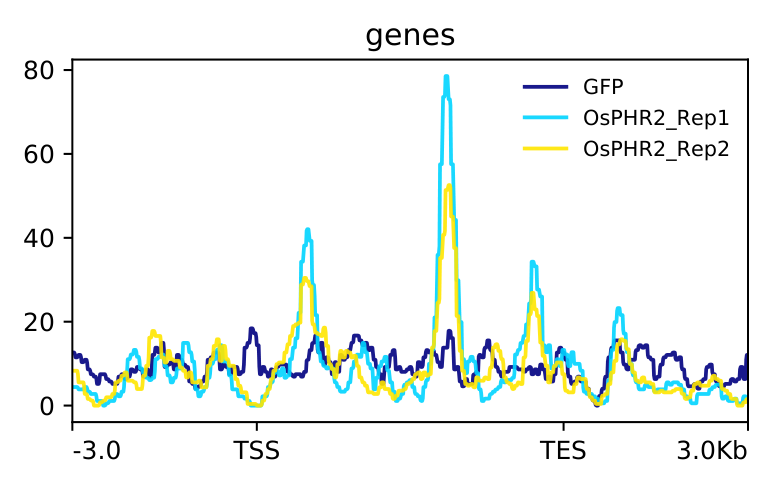
这些是我做的结果,不管是 RNA-seq 还是 DAP-seq ,差距都很大,原文材料与方法也说的不清楚,而原文使用的一些数据我使用时甚至结果都出不来.....
请问这样正常吗?
11 条回复 • 2024-04-04 20:35:22 +08:00
1
naminokoe 57 天前
v2 上懂这个的不多吧,发信问通讯作者才是正道
|
3
MrOange 57 天前
有没有一种可能,这数据不完全是真的,比如没加上某个重要的负面影响因子
|
4
deecyn 57 天前
这不就是著名的国产学术垃圾吗 https://www.bilibili.com/video/BV1Ts4y1A7wm
|
5
lekai63 57 天前 via iPhone
问通讯呗。不回复的话 也可能就是论文工厂的流水线产物
|
6
GGBond2001 57 天前
这个就是很简单的 peak 在基因功能元件上的分布图和 TSS 富集热图, 从文章的材料与方法可以知道, DAP-seq 部分的分析是外包给上海翰宇生物科技有限公司进行的. 这种图一般都是公司通过标准流程分析出来的, 一般不至于造假. 不过文章中的那个 TSS 热图确实很奇怪, 如果 GFP 是对照组的话, 得出的结论应该是 OsPHR2 与 DNA 的结合被抑制了, 但文章的结论好像恰恰相反.
|
7
GGBond2001 57 天前
|
8
UncleCAT4 OP |
9
GGBond2001 57 天前
@UncleCAT4 可以去 Biostars 或者 Stack Overflow 问一下,那边获得有效回答的可能性比较大。另外,最好贴一下你用的哪些软件及其参数,处理数据的流程。
|
10
UncleCAT4 OP @GGBond2001 我去试试
|
11
imzcg2 57 天前
不要把世界想的太美好还给她找借口,大胆的说:这就是假的,在什么资源也没有的空白房间里的论文高手生产的,出发点就很完美怎么看都完美就是不能验证
|
